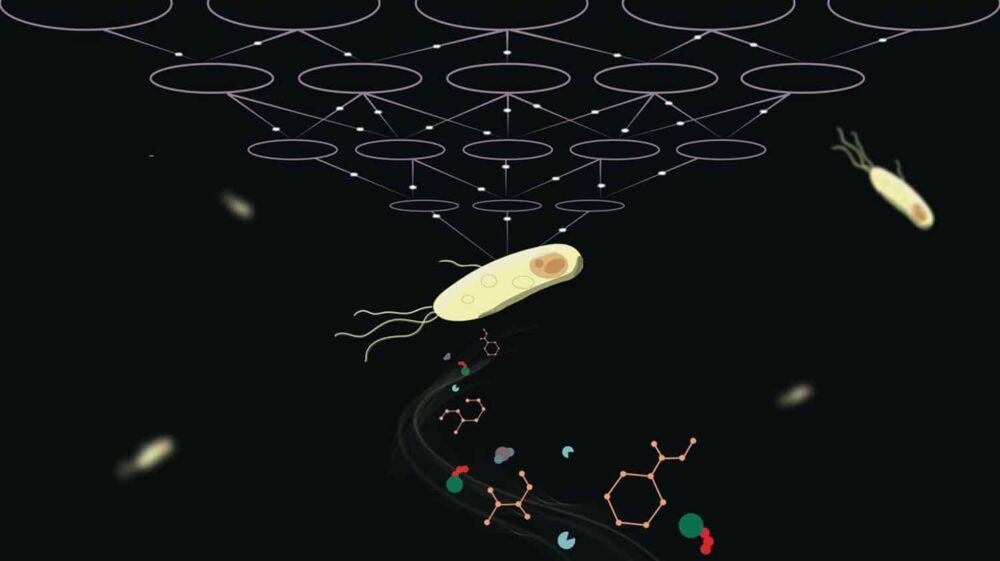
Усі живі істоти потребують обміну речовин. Те, як організм метаболізує поживні речовини, є складним процесом, і моделювання хімічних процесів, які забезпечують життя, є складним завданням.
Теоретично процедура може бути представлена математичними рівняннями з параметрами, специфічними для кожного організму. Однак практичне визначення цих параметрів – справа складна через відсутність експериментальних даних.
Вченим, як правило, потрібно багато експериментальних даних і потужності обробки, щоб знайти ці параметри. EPFL вчені запропонували обчислювальну структуру на основі глибокого навчання, яка відтворює динамічні метаболічні властивості, які спостерігаються в клітин. Структура під назвою REKINDLE може прокласти шлях до більш ефективного та точного моделювання метаболічних процесів.
Любіша Мішковіч з лабораторії біотехнології обчислювальних систем EPFL і співавтор дослідження сказав: «REKINDLE дозволить дослідницькому співтовариству скоротити обчислювальні зусилля для створення кінетичних моделей на кілька порядків. Це також допоможе висунути нові гіпотези шляхом інтеграції біохімічних даних у ці моделі, пояснення експериментальних спостережень і керування новими терапевтичними відкриттями та біотехнологічними конструкціями».
Субхем Чоудхурі, перший автор дослідження, сказав: «Головна мета метаболічного моделювання — описати поведінка клітинного метаболізму до такої міри, що розуміння та прогнозування наслідків варіацій у клітинних станах і умовах навколишнього середовища можна надійно перевірити для широкого спектру досліджень у сфері охорони здоров’я, біотехнології та системної та синтетичної біології. Ми сподіваємося, що REKINDLE полегшить створення метаболічних моделей для ширшої спільноти».
Цей метод має безпосереднє застосування в біотехнологіях, оскільки кінетичні моделі є вирішальними для численних досліджень, у тому числі щодо біопродукції, націлювання на ліки, взаємодії між мікробами та біоремедіації.
Чудхурі сказав, «REKINDLE використовує стандартні, широко використовувані бібліотеки Python, які роблять його доступним і простим у використанні. Наша головна мета в цьому дослідженні — прокласти шлях до того, щоб зробити такі зусилля з моделювання відкритими та доступними, щоб будь-хто в спільнотах синтетичної та системної біології міг використовувати їх для власних дослідницьких цілей, якими б вони не були».
Довідка з журналу:
- Чоудхурі С., Морет М., Салві П. та ін. Реконструкція кінетичних моделей для динамічних досліджень метаболізму з використанням генеративних суперницьких мереж. Nat Mach Intell 4, 710–719 (2022). DOI: 10.1038 / s42256-022-00519-y