Η ανάπτυξη φαρμάκων είναι μια πολύπλοκη και μακροχρόνια διαδικασία που περιλαμβάνει τον έλεγχο χιλιάδων υποψηφίων φαρμάκων και τη χρήση υπολογιστικών ή πειραματικών μεθόδων για την αξιολόγηση των πελατών. Σύμφωνα με τον McKinsey, ένα μεμονωμένο φάρμακο μπορεί να διαρκέσει 10 χρόνια και να κοστίσει κατά μέσο όρο 2.6 δισεκατομμύρια δολάρια για την αναγνώριση του στόχου της νόσου, τον έλεγχο φαρμάκων, την επικύρωση του στόχου φαρμάκου και την ενδεχόμενη εμπορική κυκλοφορία. Η ανακάλυψη φαρμάκων είναι το ερευνητικό συστατικό αυτού του αγωγού που παράγει υποψήφια φάρμακα με την υψηλότερη πιθανότητα να είναι αποτελεσματικά με τη μικρότερη βλάβη στους ασθενείς. Οι μέθοδοι μηχανικής μάθησης (ML) μπορούν να βοηθήσουν στον εντοπισμό κατάλληλων ενώσεων σε κάθε στάδιο της διαδικασίας ανακάλυψης φαρμάκων, με αποτέλεσμα την πιο βελτιωμένη ιεράρχηση και δοκιμή φαρμάκων, εξοικονομώντας δισεκατομμύρια σε κόστος ανάπτυξης φαρμάκων (για περισσότερες πληροφορίες, ανατρέξτε στο Τεχνητή Νοημοσύνη στην έρευνα βιοφαρμακευτικών: Ένας χρόνος εστίασης και κλίμακας).
Οι στόχοι φαρμάκων είναι συνήθως βιολογικές οντότητες που ονομάζονται πρωτεΐνες, τα δομικά στοιχεία της ζωής. Η τρισδιάστατη δομή μιας πρωτεΐνης καθορίζει πώς αλληλεπιδρά με μια φαρμακευτική ένωση. Ως εκ τούτου, η κατανόηση της τρισδιάστατης δομής της πρωτεΐνης μπορεί να προσθέσει σημαντικές βελτιώσεις στη διαδικασία ανάπτυξης φαρμάκου ελέγχοντας για ενώσεις φαρμάκων που ταιριάζουν καλύτερα στη δομή της πρωτεΐνης στόχου. Ένας άλλος τομέας όπου η πρόβλεψη της δομής των πρωτεϊνών μπορεί να είναι χρήσιμη είναι η κατανόηση της ποικιλομορφίας των πρωτεϊνών, έτσι ώστε να επιλέγουμε μόνο φάρμακα που στοχεύουν επιλεκτικά συγκεκριμένες πρωτεΐνες χωρίς να επηρεάζουν άλλες πρωτεΐνες στο σώμα (για περισσότερες πληροφορίες, ανατρέξτε στο Βελτίωση της αξιολόγησης στόχου στη βιοϊατρική έρευνα: οι συστάσεις GOT-IT). Οι ακριβείς τρισδιάστατες δομές των πρωτεϊνών-στόχων μπορούν να επιτρέψουν το σχεδιασμό φαρμάκων με υψηλότερη ειδικότητα και μικρότερη πιθανότητα διασταυρούμενων αλληλεπιδράσεων με άλλες πρωτεΐνες.
Ωστόσο, η πρόβλεψη του τρόπου αναδίπλωσης των πρωτεϊνών στην τρισδιάστατη δομή τους είναι ένα δύσκολο πρόβλημα και οι παραδοσιακές πειραματικές μέθοδοι όπως η κρυσταλλογραφία ακτίνων Χ και η φασματοσκοπία NMR μπορεί να είναι χρονοβόρες και δαπανηρές. Οι πρόσφατες πρόοδοι στις μεθόδους βαθιάς μάθησης για την έρευνα πρωτεϊνών έχουν δείξει πολλά υποσχόμενα στη χρήση νευρωνικών δικτύων για την πρόβλεψη της αναδίπλωσης πρωτεΐνης με αξιοσημείωτη ακρίβεια. Αναδιπλούμενοι αλγόριθμοι όπως AlphaFold2, ESMFold, OpenFold, να RoseTTAFold μπορεί να χρησιμοποιηθεί για τη γρήγορη κατασκευή ακριβών μοντέλων πρωτεϊνικών δομών. Δυστυχώς, αυτά τα μοντέλα είναι υπολογιστικά ακριβά στην εκτέλεση και τα αποτελέσματα μπορεί να είναι δυσκίνητα για σύγκριση στην κλίμακα χιλιάδων υποψήφιων πρωτεϊνικών δομών. Μια επεκτάσιμη λύση για τη χρήση αυτών των διαφόρων εργαλείων θα επιτρέψει σε ερευνητές και εμπορικές ομάδες Ε&Α να ενσωματώσουν γρήγορα τις πιο πρόσφατες εξελίξεις στην πρόβλεψη δομής πρωτεϊνών, να διαχειριστούν τις πειραματικές τους διαδικασίες και να συνεργαστούν με ερευνητικούς εταίρους.
Amazon Sage Maker είναι μια πλήρως διαχειριζόμενη υπηρεσία για την προετοιμασία, την κατασκευή, την εκπαίδευση και την ανάπτυξη μοντέλων ML υψηλής ποιότητας γρήγορα, συγκεντρώνοντας ένα ευρύ σύνολο δυνατοτήτων που έχουν δημιουργηθεί ειδικά για την ML. Προσφέρει ένα πλήρως διαχειριζόμενο περιβάλλον για ML, αφαιρώντας την υποδομή, τη διαχείριση δεδομένων και τις απαιτήσεις επεκτασιμότητας, ώστε να μπορείτε να εστιάσετε στη δημιουργία, την εκπαίδευση και τη δοκιμή των μοντέλων σας.
Σε αυτήν την ανάρτηση, παρουσιάζουμε μια πλήρως διαχειριζόμενη λύση ML με το SageMaker που απλοποιεί τη λειτουργία των ροών εργασιών πρόβλεψης δομής αναδίπλωσης πρωτεΐνης. Αρχικά συζητάμε τη λύση σε υψηλό επίπεδο και την εμπειρία χρήστη της. Στη συνέχεια, σας καθοδηγούμε πώς μπορείτε να ρυθμίσετε εύκολα βελτιστοποιημένες υπολογιστικές ροές εργασίας του AlphaFold2 και του OpenFold με το SageMaker. Τέλος, δείχνουμε πώς μπορείτε να παρακολουθείτε και να συγκρίνετε προβλέψεις δομής πρωτεΐνης ως μέρος μιας τυπικής ανάλυσης. Ο κώδικας για αυτήν τη λύση είναι διαθέσιμος παρακάτω Αποθετήριο GitHub.
Επισκόπηση λύσεων
Σε αυτή τη λύση, οι επιστήμονες μπορούν διαδραστικά να ξεκινήσουν πειράματα αναδίπλωσης πρωτεϊνών, να αναλύσουν την τρισδιάστατη δομή, να παρακολουθήσουν την πρόοδο της εργασίας και να παρακολουθήσουν τα πειράματα σε Στούντιο Amazon SageMaker.
Το ακόλουθο στιγμιότυπο οθόνης δείχνει μια μεμονωμένη εκτέλεση μιας ροής εργασίας αναδίπλωσης πρωτεΐνης με το Amazon SageMaker Studio. Περιλαμβάνει την απεικόνιση της τρισδιάστατης δομής σε ένα σημειωματάριο, την κατάσταση εκτέλεσης των εργασιών του SageMaker στη ροή εργασίας και συνδέσμους προς τις παραμέτρους εισόδου και τα δεδομένα εξόδου και τα αρχεία καταγραφής.
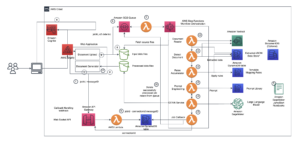
Το παρακάτω διάγραμμα απεικονίζει την αρχιτεκτονική λύσεων υψηλού επιπέδου.
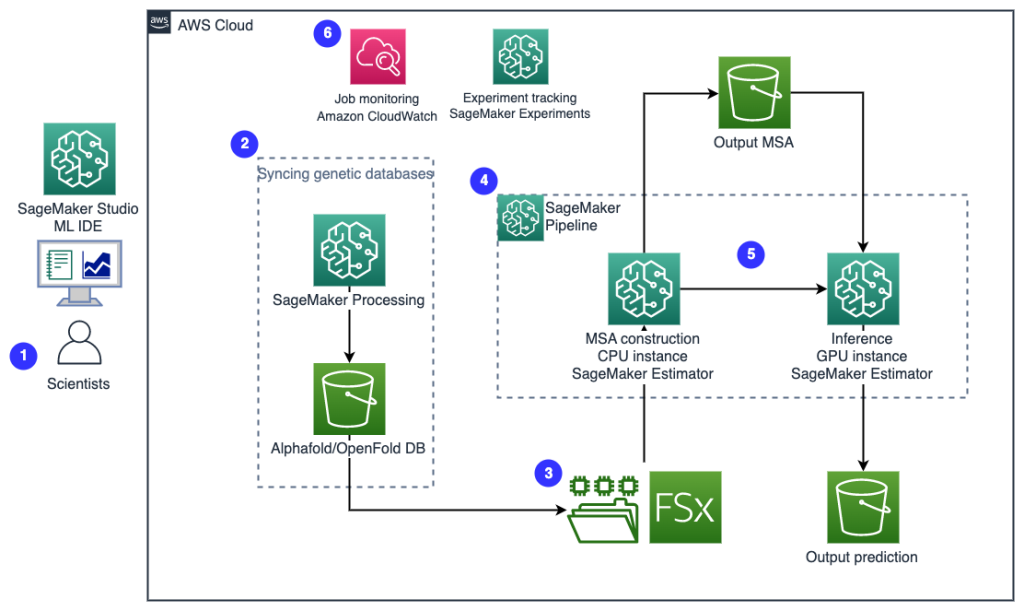
Για να κατανοήσουμε την αρχιτεκτονική, ορίζουμε πρώτα τα βασικά συστατικά ενός πειράματος αναδίπλωσης πρωτεΐνης ως εξής:
- Αρχείο ακολουθίας στόχου FASTA - Η Μορφή FASTA είναι μια μορφή βασισμένη σε κείμενο για την αναπαράσταση αλληλουχιών νουκλεοτιδίων ή αλληλουχιών αμινοξέων (πρωτεϊνών), στις οποίες τα νουκλεοτίδια ή τα αμινοξέα αναπαρίστανται χρησιμοποιώντας κωδικούς ενός γράμματος.
- Γενετικές βάσεις δεδομένων – Μια γενετική βάση δεδομένων είναι ένα ή περισσότερα σύνολα γενετικών δεδομένων που αποθηκεύονται μαζί με λογισμικό για να μπορούν οι χρήστες να ανακτούν γενετικά δεδομένα. Απαιτούνται πολλές γενετικές βάσεις δεδομένων για την εκτέλεση αλγορίθμων AlphaFold και OpenFold, όπως π.χ BFD, MGnify, ΠΣΠ70, ΠΠ, ακολουθίες ΠΣΠ, UniRef30 (FKA UniClust30), UniProt, να UniRef90.
- Στοίχιση πολλαπλών ακολουθιών (MSA) - Μια στοίχιση ακολουθίας είναι ένας τρόπος διάταξης των πρωτογενών αλληλουχιών μιας πρωτεΐνης για τον εντοπισμό περιοχών ομοιότητας που μπορεί να είναι συνέπεια λειτουργικών, δομικών ή εξελικτικών σχέσεων μεταξύ των αλληλουχιών. Οι δυνατότητες εισαγωγής για προβλέψεις περιλαμβάνουν δεδομένα MSA.
- Πρόβλεψη δομής πρωτεΐνης – Η δομή των ακολουθιών στόχων εισόδου προβλέπεται με αναδιπλούμενους αλγόριθμους όπως AlphaFold2 και OpenFold που χρησιμοποιούν μια αρχιτεκτονική μετασχηματιστή πολλαπλών τροχιών, εκπαιδευμένη σε γνωστά πρότυπα πρωτεϊνών.
- Οπτικοποίηση και μετρήσεις – Οραματιστείτε την τρισδιάστατη δομή με το py3Dmol βιβλιοθήκη ως διαδραστική τρισδιάστατη απεικόνιση. Μπορείτε να χρησιμοποιήσετε μετρήσεις για να αξιολογήσετε και να συγκρίνετε προβλέψεις δομής, κυρίως απόκλιση ρίζας-μέσος τετραγώνου (RMSD) και Βαθμολογία μοντελοποίησης προτύπου (ΤΜ-βαθμολογία)
Η ροή εργασίας περιέχει τα ακόλουθα βήματα:
- Οι επιστήμονες χρησιμοποιούν το διαδικτυακό SageMaker ML IDE για να εξερευνήσουν τη βάση κώδικα, να δημιουργήσουν ροές εργασιών ανάλυσης ακολουθίας πρωτεϊνών σε σημειωματάρια του SageMaker Studio και να εκτελέσουν αγωγούς αναδίπλωσης πρωτεΐνης μέσω της γραφικής διεπαφής χρήστη στο SageMaker Studio ή στο SageMaker SDK.
- Οι βάσεις δεδομένων γενετικών και δομικών δεδομένων που απαιτούνται από το AlphaFold και το OpenFold πραγματοποιούνται λήψη πριν από τη ρύθμιση του pipeline χρησιμοποιώντας Επεξεργασία Amazon SageMaker, μια εφήμερη δυνατότητα υπολογισμού για επεξεργασία δεδομένων ML, σε ένα Απλή υπηρεσία αποθήκευσης Amazon (Amazon S3) κάδος. Με το SageMaker Processing, μπορείτε να εκτελέσετε μια μακροχρόνια εργασία με σωστό υπολογισμό χωρίς να ρυθμίσετε κανένα σύμπλεγμα υπολογιστών και χώρο αποθήκευσης και χωρίς να χρειάζεται να τερματίσετε τη λειτουργία του συμπλέγματος. Τα δεδομένα αποθηκεύονται αυτόματα σε μια καθορισμένη θέση του κάδου S3.
- An Amazon FSx για λάμψη έχει ρυθμιστεί το σύστημα αρχείων, με το αποθετήριο δεδομένων να είναι η θέση του κάδου S3 όπου αποθηκεύονται οι βάσεις δεδομένων. Το FSx for Luster μπορεί να κλιμακωθεί σε εκατοντάδες GB/s απόδοσης και εκατομμύρια IOPS με ανάκτηση αρχείων χαμηλής καθυστέρησης. Κατά την εκκίνηση μιας εργασίας εκτιμητή, το SageMaker προσαρτά το σύστημα αρχείων FSx for Luster στο σύστημα αρχείων της παρουσίας και, στη συνέχεια, ξεκινά το σενάριο.
- Αγωγοί Amazon SageMaker χρησιμοποιείται για την ενορχήστρωση πολλαπλών σειρών αλγορίθμων αναδίπλωσης πρωτεϊνών. Το SageMaker Pipelines προσφέρει μια επιθυμητή οπτική διεπαφή για διαδραστική υποβολή εργασιών, ιχνηλασιμότητα της προόδου και επαναληψιμότητα.
- Μέσα σε μια διοχέτευση, δύο υπολογιστικά βαρείς αλγόριθμοι αναδίπλωσης πρωτεϊνών — AlphaFold και OpenFold — εκτελούνται με εκτιμητές SageMaker. Αυτή η διαμόρφωση υποστηρίζει την τοποθέτηση ενός συστήματος αρχείων FSx for Luster για αναζήτηση βάσεων δεδομένων υψηλής απόδοσης στους αλγόριθμους. Μια απλή εκτέλεση συμπερασμάτων χωρίζεται σε δύο βήματα: ένα βήμα κατασκευής MSA που χρησιμοποιεί μια βέλτιστη παρουσία CPU και ένα βήμα πρόβλεψης δομής χρησιμοποιώντας μια παρουσία GPU. Αυτά τα υποβήματα, όπως το SageMaker Processing στο Βήμα 2, είναι εφήμερα, κατ' απαίτηση και πλήρως διαχειριζόμενα. Έξοδοι εργασιών, όπως αρχεία MSA, προβλεπόμενα αρχεία δομής pdb και άλλα αρχεία μεταδεδομένων αποθηκεύονται σε μια καθορισμένη θέση S3. Ένας αγωγός μπορεί να σχεδιαστεί για να εκτελεί έναν αλγόριθμο αναδίπλωσης πρωτεΐνης ή να εκτελεί τόσο το AlphaFold όσο και το OpenFold μετά από μια κοινή κατασκευή MSA.
- Οι σειρές της πρόβλεψης αναδίπλωσης πρωτεΐνης παρακολουθούνται αυτόματα από Πειράματα Amazon SageMaker για περαιτέρω ανάλυση και σύγκριση. Τα αρχεία καταγραφής εργασιών διατηρούνται amazoncloudwatch για παρακολούθηση.
Προϋποθέσεις
Για να ακολουθήσετε αυτήν την ανάρτηση και να εκτελέσετε αυτήν τη λύση, πρέπει να έχετε ολοκληρώσει αρκετές προϋποθέσεις. Αναφέρομαι στο Αποθετήριο GitHub για λεπτομερή επεξήγηση κάθε βήματος.
Εκτελέστε αναδίπλωση πρωτεΐνης στο SageMaker
Χρησιμοποιούμε τις πλήρως διαχειριζόμενες δυνατότητες του SageMaker για να εκτελέσουμε υπολογιστικά βαριές εργασίες αναδίπλωσης πρωτεϊνών χωρίς πολλά έξοδα υποδομής. Το SageMaker χρησιμοποιεί εικόνες κοντέινερ για την εκτέλεση προσαρμοσμένων σεναρίων για γενική επεξεργασία δεδομένων, εκπαίδευση και φιλοξενία. Μπορείτε εύκολα να ξεκινήσετε μια εφήμερη εργασία κατ' απαίτηση που εκτελεί ένα πρόγραμμα με μια εικόνα κοντέινερ με μερικές γραμμές του SageMaker SDK χωρίς αυτοδιαχείριση υπολογιστικής υποδομής. Συγκεκριμένα, η εργασία εκτιμητή SageMaker παρέχει ευελιξία όσον αφορά την επιλογή της εικόνας κοντέινερ, του σεναρίου εκτέλεσης και της διαμόρφωσης παρουσίας και υποστηρίζει μεγάλη ποικιλία επιλογών αποθήκευσης, συμπεριλαμβανομένων συστημάτων αρχείων όπως το FSx for Lustre. Το παρακάτω διάγραμμα απεικονίζει αυτήν την αρχιτεκτονική.
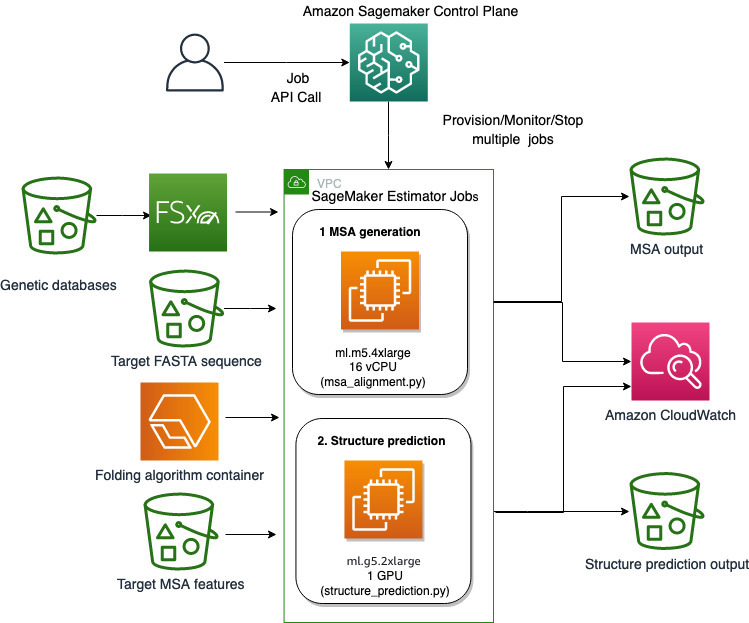
Οι αναδιπλούμενοι αλγόριθμοι όπως ο AlphaFold και ο OpenFold χρησιμοποιούν μια αρχιτεκτονική μετασχηματιστή πολλαπλών τροχιών που έχει εκπαιδευτεί σε γνωστά πρότυπα πρωτεϊνών για την πρόβλεψη της δομής άγνωστων πεπτιδικών ακολουθιών. Αυτές οι προβλέψεις μπορούν να εκτελεστούν σε στιγμιότυπα GPU για να παρέχουν την καλύτερη απόδοση και τη χαμηλότερη καθυστέρηση. Ωστόσο, τα χαρακτηριστικά εισόδου για αυτές τις προβλέψεις περιλαμβάνουν δεδομένα MSA. Οι αλγόριθμοι MSA εξαρτώνται από την CPU και μπορεί να απαιτούν αρκετές ώρες χρόνου επεξεργασίας.
Η εκτέλεση τόσο των βημάτων MSA όσο και των βημάτων πρόβλεψης δομής στο ίδιο υπολογιστικό περιβάλλον μπορεί να είναι οικονομικά αναποτελεσματική, επειδή οι ακριβοί πόροι GPU παραμένουν αδρανείς όσο εκτελείται το βήμα MSA. Επομένως, βελτιστοποιούμε τη ροή εργασίας σε δύο βήματα. Αρχικά, εκτελούμε μια εργασία εκτιμητή SageMaker σε μια παρουσία της CPU ειδικά για τον υπολογισμό της ευθυγράμμισης MSA δεδομένης μιας συγκεκριμένης ακολουθίας εισόδου FASTA και μιας γενετικής βάσης δεδομένων πηγής. Στη συνέχεια, εκτελούμε μια εργασία εκτιμητή SageMaker σε μια παρουσία GPU για να προβλέψουμε τη δομή της πρωτεΐνης με μια δεδομένη στοίχιση MSA εισόδου και έναν αναδιπλούμενο αλγόριθμο όπως το AlphaFold ή το OpenFold.
Εκτελέστε τη γενιά MSA
Για τον υπολογισμό MSA, περιλαμβάνουμε ένα προσαρμοσμένο σενάριο run_create_alignment.sh και create_alignments.py σενάριο που υιοθετείται από την υπάρχουσα πηγή πρόβλεψης AlphaFold run_alphafold.py. Σημειώστε ότι αυτό το σενάριο ενδέχεται να χρειαστεί να ενημερωθεί εάν ενημερωθεί ο κώδικας AlphaFold προέλευσης. Το προσαρμοσμένο σενάριο παρέχεται στον εκτιμητή SageMaker μέσω λειτουργία σεναρίου. Τα βασικά στοιχεία της εικόνας του κοντέινερ, η υλοποίηση της λειτουργίας σεναρίου και η ρύθμιση μιας εργασίας εκτιμητή SageMaker αποτελούν επίσης μέρος του επόμενου βήματος της εκτέλεσης αναδιπλούμενων αλγορίθμων και περιγράφονται περαιτέρω στην επόμενη ενότητα.
Εκτελέστε το AlphaFold
Ξεκινάμε εκτελώντας μια πρόβλεψη δομής AlphaFold με μία μόνο αλληλουχία πρωτεΐνης χρησιμοποιώντας το SageMaker. Η εκτέλεση μιας εργασίας AlphaFold περιλαμβάνει τρία απλά βήματα, όπως φαίνεται στο 01-run_stepbystep.ipynb. Αρχικά, χτίζουμε μια εικόνα κοντέινερ Docker βασισμένη σε AlphaFold's Dockerfile για να μπορούμε κι εμείς εκτελέστε το AlphaFold στο SageMaker. Δεύτερον, κατασκευάζουμε το σενάριο run_alphafold.sh που καθοδηγεί τον τρόπο εκτέλεσης του AlphaFold. Τρίτον, κατασκευάζουμε και τρέχουμε ένα Εκτιμητής SageMaker με το σενάριο, το κοντέινερ, τον τύπο παρουσίας, τα δεδομένα και τη διαμόρφωση για την εργασία.
Εικόνα κοντέινερ
Η απαίτηση χρόνου εκτέλεσης για μια εικόνα κοντέινερ για εκτέλεση του AlphaFold (και OpenFold) στο SageMaker μπορεί να απλοποιηθεί σημαντικά με το Dockerfile του AlphaFold. Χρειάζεται μόνο να προσθέσουμε μια χούφτα απλών επιπέδων από πάνω για να εγκαταστήσουμε μια βιβλιοθήκη Python ειδικά για το SageMaker, έτσι ώστε μια εργασία SageMaker να μπορεί να επικοινωνεί με την εικόνα του κοντέινερ. Δείτε τον παρακάτω κώδικα:
Σενάριο εισαγωγής
Στη συνέχεια παρέχουμε το σενάριο run_alphafold.sh που τρέχει run_alphafold.py από το αποθετήριο AlphaFold που βρίσκεται αυτήν τη στιγμή στο κοντέινερ /app/alphafold/run_alphafold.py. Όταν εκτελείται αυτό το σενάριο, η θέση των γενετικών βάσεων δεδομένων και η ακολουθία εισόδου FASTA θα συμπληρώνονται από το SageMaker ως μεταβλητές περιβάλλοντος (SM_CHANNEL_GENETIC και SM_CHANNEL_FASTA, αντίστοιχα). Για περισσότερες πληροφορίες, ανατρέξτε στο Διαμόρφωση δεδομένων εισόδου.
Εργασία εκτιμητή
Στη συνέχεια, δημιουργούμε μια εργασία χρησιμοποιώντας έναν εκτιμητή SageMaker με τα ακόλουθα βασικά ορίσματα εισαγωγής, τα οποία καθοδηγούν το SageMaker να εκτελέσει ένα συγκεκριμένο σενάριο χρησιμοποιώντας ένα καθορισμένο κοντέινερ με τον τύπο ή τον αριθμό παρουσίας, την επιλογή δικτύωσης της επιλογής σας και άλλες παραμέτρους για την εργασία. vpc_subnet_ids και security_group_ids δώστε εντολή στην εργασία να εκτελεστεί μέσα σε ένα συγκεκριμένο VPC όπου βρίσκεται το σύστημα αρχείων FSx for Luster, ώστε να μπορούμε να προσαρτήσουμε και να αποκτήσουμε πρόσβαση στο σύστημα αρχείων στην εργασία SageMaker. Η διαδρομή εξόδου αναφέρεται σε μια θέση κάδου S3 όπου το τελικό προϊόν του AlphaFold θα μεταφορτωθεί αυτόματα στο τέλος μιας επιτυχημένης εργασίας από το SageMaker. Εδώ ορίζουμε και μια παράμετρο DB_PRESET, για παράδειγμα, για μεταβίβαση και πρόσβαση εντός run_alphafold.sh ως περιβαλλοντική μεταβλητή κατά τη διάρκεια του χρόνου εκτέλεσης. Δείτε τον παρακάτω κώδικα:
from sagemaker.estimator import Estimator
alphafold_image_uri=f'{account}.dkr.ecr.{region}.amazonaws.com/sagemaker-studio-alphafold:v2.3.0'
instance_type='ml.g5.2xlarge'
instance_count=1
vpc_subnet_ids=['subnet-xxxxxxxxx'] # okay to use a default VPC
security_group_ids=['sg-xxxxxxxxx']
env={'DB_PRESET': db_preset} # <full_dbs|reduced_dbs>
output_path='s3://%s/%s/job-output/'%(default_bucket, prefix) estimator_alphafold = Estimator(
source_dir='src', # directory where run_alphafold.sh and other runtime files locate
entry_point='run_alphafold.sh', # our script that runs /app/alphafold/run_alphafold.py
image_uri=alphafold_image_uri, # container image to use
instance_count=instance_count, #
instance_type=instance_type,
subnets=vpc_subnet_ids,
security_group_ids=security_group_ids,
environment=env,
output_path=output_path,
...)Τέλος, συγκεντρώνουμε τα δεδομένα και ενημερώνουμε την εργασία πού βρίσκονται. ο fasta Το κανάλι δεδομένων ορίζεται ως μια είσοδος δεδομένων S3 που θα ληφθεί από μια θέση S3 στην παρουσία υπολογιστών στην αρχή της εργασίας. Αυτό επιτρέπει μεγάλη ευελιξία στη διαχείριση και τον καθορισμό της ακολουθίας εισόδου. Από την άλλη πλευρά, το genetic Το κανάλι δεδομένων ορίζεται ως α FileSystemInput που θα τοποθετηθεί στο στιγμιότυπο στην αρχή της εργασίας. Η χρήση ενός συστήματος αρχείων FSx for Luster ως ένας τρόπος για να φέρετε δεδομένα κοντά στα 3 TB αποφεύγει την επανειλημμένη λήψη δεδομένων από έναν κάδο S3 σε μια παρουσία υπολογιστών. Καλούμε το .fit μέθοδος έναρξης μιας εργασίας AlphaFold:
from sagemaker.inputs import FileSystemInput
file_system_id='fs-xxxxxxxxx'
fsx_mount_id='xxxxxxxx'
file_system_directory_path=f'/{fsx_mount_id}/{prefix}/alphafold-genetic-db' # should be the full prefix from the S3 data repository file_system_access_mode='ro' # Specify the access mode (read-only)
file_system_type='FSxLustre' # Specify your file system type genetic_db = FileSystemInput(
file_system_id=file_system_id,
file_system_type=file_system_type,
directory_path=file_system_directory_path,
file_system_access_mode=file_system_access_mode) s3_fasta=sess.upload_data(path='sequence_input/T1030.fasta', # FASTA location locally
key_prefix='alphafoldv2/sequence_input') # S3 prefix. Bucket is sagemaker default bucket
fasta = sagemaker.inputs.TrainingInput(s3_fasta,
distribution='FullyReplicated',
s3_data_type='S3Prefix',
input_mode='File')
data_channels_alphafold = {'genetic': genetic_db, 'fasta': fasta} estimator_alphafold.fit(inputs=data_channels_alphafold,
wait=False) # wait=False gets the cell back in the notebook; set to True to see the logs as the job progressesΑυτό είναι. Μόλις υποβάλαμε μια εργασία στο SageMaker για να τρέξει το AlphaFold. Τα αρχεία καταγραφής και η έξοδος συμπεριλαμβανομένων των αρχείων πρόβλεψης .pdb θα εγγραφούν στο Amazon S3.
Εκτελέστε το OpenFold
Η εκτέλεση του OpenFold στο SageMaker ακολουθεί ένα παρόμοιο μοτίβο, όπως φαίνεται στο δεύτερο μισό του 01-run_stepbystep.ipynb. Προσθέτουμε πρώτα ένα απλό επίπεδο για να αποκτήσουμε τη βιβλιοθήκη του SageMaker για να κάνουμε την εικόνα του κοντέινερ συμβατή με το SageMaker πάνω από το OpenFold Dockerfile. Δεύτερον, κατασκευάζουμε ένα run_openfold.sh ως σημείο εισόδου για την εργασία SageMaker. Σε run_openfold.sh, τρέχουμε το run_pretrained_openfold.py από το OpenFold, που είναι διαθέσιμο στην εικόνα του κοντέινερ με τις ίδιες γενετικές βάσεις δεδομένων που κατεβάσαμε για τα βάρη μοντέλων AlphaFold και OpenFold (--openfold_checkpoint_path). Όσον αφορά τις θέσεις δεδομένων εισόδου, εκτός από το κανάλι γενετικών βάσεων δεδομένων και το κανάλι FASTA, εισάγουμε ένα τρίτο κανάλι, SM_CHANNEL_PARAM, έτσι ώστε να μπορούμε να περάσουμε με ευελιξία τα βάρη του μοντέλου της επιλογής από την κατασκευή του εκτιμητή όταν ορίζουμε και υποβάλλουμε μια εργασία. Με τον εκτιμητή SageMaker, μπορούμε εύκολα να υποβάλουμε εργασίες με διαφορετικές entry_point, image_uri, environment, inputsκαι άλλες διαμορφώσεις για το OpenFold με την ίδια υπογραφή. Για το κανάλι δεδομένων, προσθέτουμε ένα νέο κανάλι, param, ως είσοδο Amazon S3 μαζί με τη χρήση των ίδιων γενετικών βάσεων δεδομένων από το σύστημα αρχείων FSx for Luster και το αρχείο FASTA από το Amazon S3. Αυτό, πάλι, μας επιτρέπει να προσδιορίσουμε εύκολα το βάρος του μοντέλου που θα χρησιμοποιήσουμε από την κατασκευή εργασίας. Δείτε τον παρακάτω κώδικα:
s3_param=sess.upload_data(path='openfold_params/finetuning_ptm_2.pt',
key_prefix=f'{prefix}/openfold_params')
param = sagemaker.inputs.TrainingInput(s3_param,
distribution="FullyReplicated",
s3_data_type="S3Prefix",
input_mode='File') data_channels_openfold = {"genetic": genetic_db, 'fasta': fasta, 'param': param} estimator_openfold.fit(inputs=data_channels_openfold,
wait=False)Για να αποκτήσουμε πρόσβαση στην τελική έξοδο μετά την ολοκλήρωση της εργασίας, εκτελούμε τις ακόλουθες εντολές:
!aws s3 cp {estimator_openfold.model_data} openfold_output/model.tar.gz
!tar zxfv openfold_output/model.tar.gz -C openfold_output/Απόδοση χρόνου εκτέλεσης
Ο παρακάτω πίνακας δείχνει την εξοικονόμηση κόστους 57% και 51% για το AlphaFold και το OpenFold, αντίστοιχα, διαιρώντας τους αλγόριθμους ευθυγράμμισης και αναδίπλωσης MSA σε δύο εργασίες σε σύγκριση με μία εργασία υπολογισμού. Μας επιτρέπει να κάνουμε τον υπολογισμό με το σωστό μέγεθος για κάθε εργασία: ml.m5.4xlarge για ευθυγράμμιση MSA και ml.g5.2xlarge για AlphaFold και OpenFold.
| λεπτομέρειες δουλειά | Τύπος συμβολής | Εισαγάγετε την ακολουθία FASTA | Διάρκεια | Κόστος |
| Ευθυγράμμιση MSA + OpenFold | ml.g5.4xμεγάλο | T1030 | 50 λεπτά | $1.69 |
| Ευθυγράμμιση MSA + AlphaFold | ml.g5.4xμεγάλο | T1030 | 65 λεπτά | $2.19 |
| Ευθυγράμμιση MSA | ml.m5.4xlarge | T1030 | 46 λεπτά | $0.71 |
| OpenFold | ml.g5.2xμεγάλο | T1030 | 6 λεπτά | $0.15 |
| AlphaFold | ml.g5.2xμεγάλο | T1030 | 21 λεπτά | $0.53 |
Δημιουργήστε μια επαναλαμβανόμενη ροή εργασίας χρησιμοποιώντας το SageMaker Pipelines
Με το SageMaker Pipelines, μπορούμε να δημιουργήσουμε μια ροή εργασίας ML που φροντίζει για τη διαχείριση των δεδομένων μεταξύ των βημάτων, την ενορχήστρωση των εκτελέσεών τους και την καταγραφή. Το SageMaker Pipelines μας παρέχει επίσης μια διεπαφή χρήστη για να οπτικοποιήσουμε τη διοχέτευσή μας και να εκτελέσουμε εύκολα τη ροή εργασίας ML.
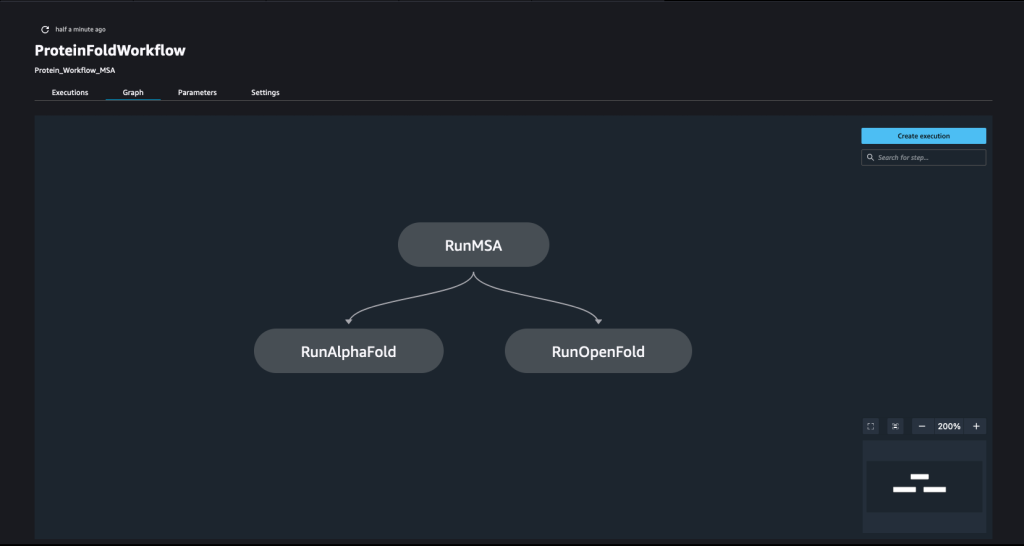
Ένας αγωγός δημιουργείται με το χτένισμα ενός αριθμού από βήματα. Σε αυτόν τον αγωγό, συνδυάζουμε τρία εκπαιδευτικά βήματα, τα οποία απαιτούν έναν εκτιμητή SageMaker. Οι εκτιμητές που ορίζονται σε αυτό το σημειωματάριο είναι πολύ παρόμοιοι με αυτούς που ορίζονται στο 01-run_stepbystep.ipynb, με την εξαίρεση ότι χρησιμοποιούμε τοποθεσίες Amazon S3 για να δείξουμε τις εισόδους και τις εξόδους μας. Οι δυναμικές μεταβλητές επιτρέπουν στο SageMaker Pipelines να εκτελεί τα βήματα το ένα μετά το άλλο και επίσης επιτρέπουν στον χρήστη να δοκιμάσει ξανά τα αποτυχημένα βήματα. Το ακόλουθο στιγμιότυπο οθόνης δείχνει ένα Κατευθυνόμενο Ακυκλικό Γράφημα (DAG), το οποίο παρέχει πληροφορίες σχετικά με τις απαιτήσεις και τις σχέσεις μεταξύ κάθε βήματος του αγωγού μας.
Δυναμικές μεταβλητές
Το SageMaker Pipelines είναι σε θέση να λαμβάνει εισόδους από τους χρήστες στην αρχή κάθε εκτέλεσης του αγωγού. Ορίζουμε τις ακόλουθες δυναμικές μεταβλητές, τις οποίες θα θέλαμε να αλλάξουμε κατά τη διάρκεια κάθε πειράματος:
- FastaInputS3URI – Amazon S3 URI του αρχείου FASTA που έχει μεταφορτωθεί μέσω SDK, Boto3 ή μη αυτόματα.
- FastFileName – Όνομα του αρχείου FASTA.
- db_preset – Επιλογή μεταξύ
full_dbsorreduced_dbs. - MaxTemplateDate – Το βήμα MSA του AlphaFold θα αναζητήσει τα διαθέσιμα πρότυπα πριν από την ημερομηνία που καθορίζεται από αυτήν την παράμετρο.
- ModelPreset – Επιλέξτε μεταξύ μοντέλων AlphaFold συμπεριλαμβανομένων
monomer,monomer_casp14,monomer_ptm, ναmultimer. - NumMultimerPredictionsPerModel – Αριθμός σπόρων προς εκτέλεση ανά μοντέλο κατά τη χρήση του συστήματος πολυμερών.
- InferenceInstanceType – Τύπος στιγμιότυπου που θα χρησιμοποιηθεί για βήματα συμπερασμάτων (τόσο AlphaFold όσο και OpenFold). Η προεπιλεγμένη τιμή είναι ml.g5.2xlarge.
- MSAInstanceType – Τύπος στιγμιότυπου που θα χρησιμοποιηθεί για το βήμα MSA. Η προεπιλεγμένη τιμή είναι ml.m5.4xlarge.
Δείτε τον ακόλουθο κώδικα:
fasta_file = ParameterString(name="FastaFileName")
fasta_input = ParameterString(name="FastaInputS3URI")
pipeline_db_preset = ParameterString(name="db_preset",
default_value='full_dbs',
enum_values=['full_dbs', 'reduced_dbs'])
max_template_date = ParameterString(name="MaxTemplateDate")
model_preset = ParameterString(name="ModelPreset")
num_multimer_predictions_per_model = ParameterString(name="NumMultimerPredictionsPerModel")
msa_instance_type = ParameterString(name="MSAInstanceType", default_value='ml.m5.4xlarge')
instance_type = ParameterString(name="InferenceInstanceType", default_value='ml.g5.2xlarge')Ένας αγωγός SageMaker κατασκευάζεται ορίζοντας μια σειρά βημάτων και στη συνέχεια συνδέοντάς τα με μια συγκεκριμένη σειρά όπου η έξοδος ενός προηγούμενου βήματος γίνεται η είσοδος στο επόμενο βήμα. Τα βήματα μπορούν να εκτελεστούν παράλληλα και να οριστούν ότι έχουν εξάρτηση από ένα προηγούμενο βήμα. Σε αυτήν τη γραμμή, ορίζουμε ένα βήμα MSA, το οποίο είναι η εξάρτηση για ένα βήμα εξαγωγής συμπερασμάτων AlphaFold και βήμα συμπεράσματος OpenFold που εκτελούνται παράλληλα. Δείτε τον παρακάτω κώδικα:
step_msa = TrainingStep(
name="RunMSA",
step_args=pipeline_msa_args,
) step_alphafold = TrainingStep(
name="RunAlphaFold",
step_args=pipeline_alphafold_default_args,
)
step_alphafold.add_depends_on([step_msa]) step_openfold = TrainingStep(
name="RunOpenFold",
step_args=pipeline_openfold_args,
)
step_openfold.add_depends_on([step_msa]Για να συνδυάσουμε όλα τα βήματα, καλούμε το Pipeline τάξη και παρέχετε ένα όνομα διοχέτευσης, μεταβλητές εισόδου αγωγού και τα επιμέρους βήματα:
pipeline_name = f"ProteinFoldWorkflow"
pipeline = Pipeline(
name=pipeline_name,
parameters=[
fasta_input,
instance_type,
msa_instance_type,
pipeline_db_preset
],
steps=[step_msa, step_alphafold, step_openfold],
) pipeline.upsert(role_arn=role, # run this if it's the first time setting up the pipeline
description='Protein_Workflow_MSA')Εκτελέστε τον αγωγό
Στο τελευταίο κελί του τετραδίου 02-define_pipeline.ipynb, δείχνουμε πώς να εκτελέσετε μια διοχέτευση χρησιμοποιώντας το SageMaker SDK. Οι δυναμικές μεταβλητές που περιγράψαμε προηγουμένως παρέχονται ως εξής:
!mkdir ./sequence_input/
!curl 'https://www.predictioncenter.org/casp14/target.cgi?target=T1030&view=sequence' > ./sequence_input/T1030.fasta
fasta_file_name = 'T1030.fasta' pathName = f'./sequence_input/{fasta_file_name}'
s3_fasta=sess.upload_data(path=pathName,
key_prefix='alphafoldv2/sequence_input') PipelineParameters={ 'FastaInputS3URI':s3_fasta, 'db_preset': 'full_dbs', 'FastaFileName': fasta_file_name, 'MaxTemplateDate': '2020-05-14', 'ModelPreset': 'monomer', 'NumMultimerPredictionsPerModel': '5', 'InferenceInstanceType':'ml.g5.2xlarge', 'MSAInstanceType':'ml.m5.4xlarge'
}
execution = pipeline.start(execution_display_name='SDK-Executetd',
execution_description='This pipeline was executed via SageMaker SDK',
parameters=PipelineParameters
)Παρακολούθηση πειραμάτων και σύγκριση πρωτεϊνικών δομών
Για το πείραμά μας, χρησιμοποιούμε ένα παράδειγμα αλληλουχίας πρωτεΐνης από το CASP14 ανταγωνισμού, ο οποίος παρέχει έναν ανεξάρτητο μηχανισμό για την αξιολόγηση των μεθόδων μοντελοποίησης της δομής των πρωτεϊνών. Ο ΣΤΟΧΟΣ T1030 προέρχεται από την πρωτεΐνη PDB 6P00 και έχει 237 αμινοξέα στην πρωτογενή αλληλουχία. Εκτελούμε τη διοχέτευση του SageMaker για να προβλέψουμε τη δομή πρωτεΐνης αυτής της ακολουθίας εισόδου με τους αλγόριθμους OpenFold και AlphaFold.
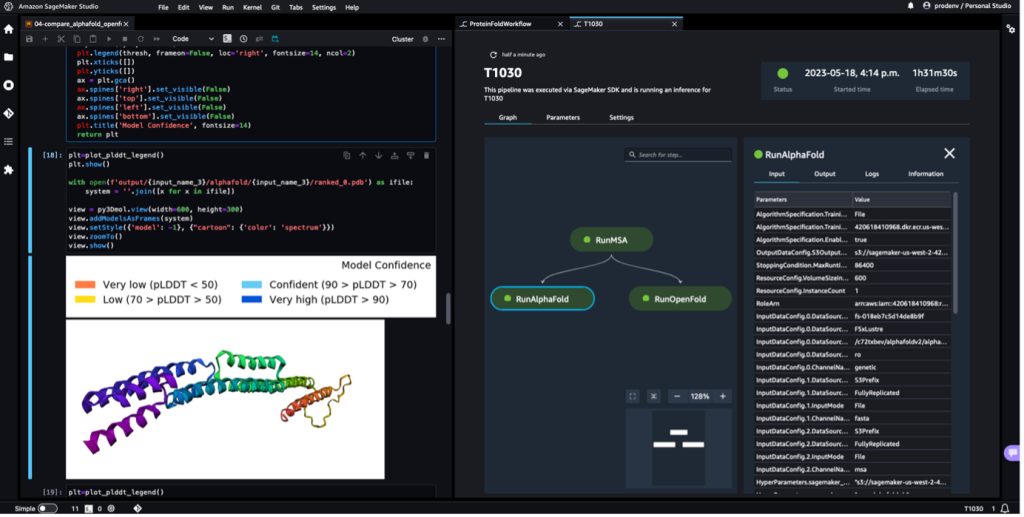
Όταν ολοκληρωθεί η διοχέτευση, πραγματοποιούμε λήψη των προβλεπόμενων αρχείων .pdb από κάθε αναδιπλούμενη εργασία και οπτικοποιούμε τη δομή στο σημειωματάριο χρησιμοποιώντας py3Dmol, όπως στο σημειωματάριο 04-compare_alphafold_openfold.ipynb.
Το ακόλουθο στιγμιότυπο οθόνης δείχνει την πρόβλεψη από την εργασία πρόβλεψης AlphaFold.
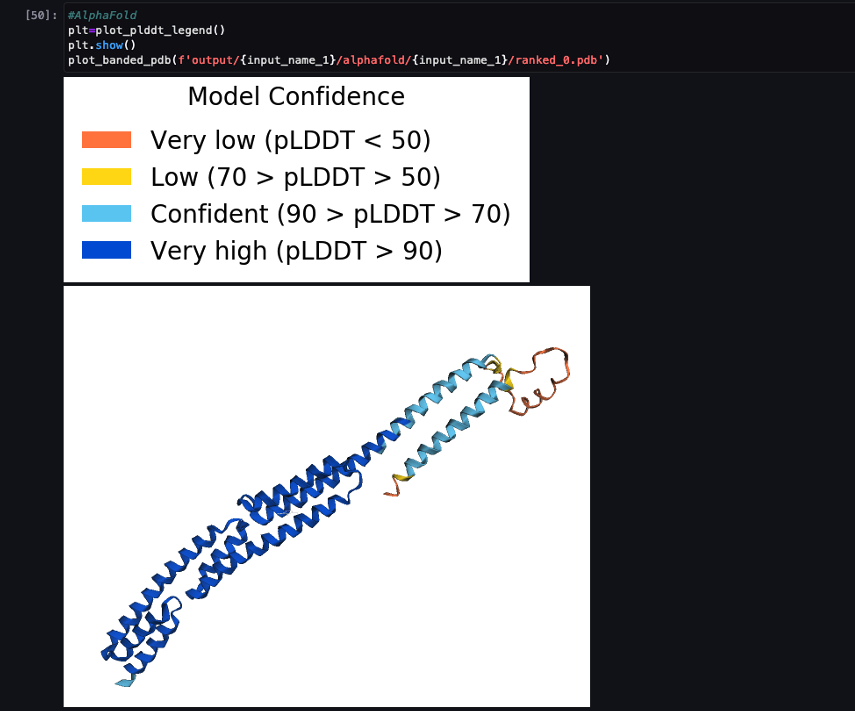
Η προβλεπόμενη δομή συγκρίνεται με τη γνωστή βασική δομή αναφοράς της με τον κώδικα PDB 6 poo αρχειοθετημένο σε RCSB. Αναλύουμε την απόδοση πρόβλεψης σε σχέση με τον βασικό κωδικό PDB 6poo με τρεις μετρήσεις: RMSD, RMSD με υπέρθεση και βαθμολογία μοντελοποίησης προτύπου, όπως περιγράφεται στο Σύγκριση δομών.
| . | Ακολουθία εισαγωγής | Συγκριτικά με | RMSD | RMSD με υπέρθεση | Βαθμολογία μοντελοποίησης προτύπου |
| AlphaFold | T1030 | 6 poo | 247.26 | 3.87 | 0.3515 |
Οι αλγόριθμοι αναδίπλωσης συγκρίνονται τώρα μεταξύ τους για πολλαπλές ακολουθίες FASTA: T1030, T1090, να T1076. Οι νέες αλληλουχίες στόχου μπορεί να μην έχουν τη βασική δομή pdb σε βάσεις δεδομένων αναφοράς και επομένως είναι χρήσιμο να συγκρίνετε τη μεταβλητότητα μεταξύ αναδιπλούμενων αλγορίθμων.
| . | Ακολουθία εισαγωγής | Συγκριτικά με | RMSD | RMSD με υπέρθεση | Βαθμολογία μοντελοποίησης προτύπου |
| AlphaFold | T1030 | OpenFold | 73.21 | 24.8 | 0.0018 |
| AlphaFold | T1076 | OpenFold | 38.71 | 28.87 | 0.0047 |
| AlphaFold | T1090 | OpenFold | 30.03 | 20.45 | 0.005 |
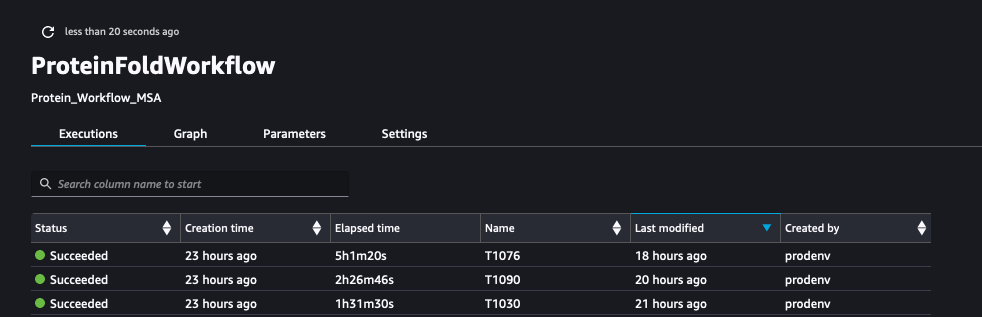
Το παρακάτω στιγμιότυπο οθόνης δείχνει τις εκτελέσεις του ProteinFoldWorkflow για τις τρεις ακολουθίες εισόδου FASTA με το SageMaker Pipeline:
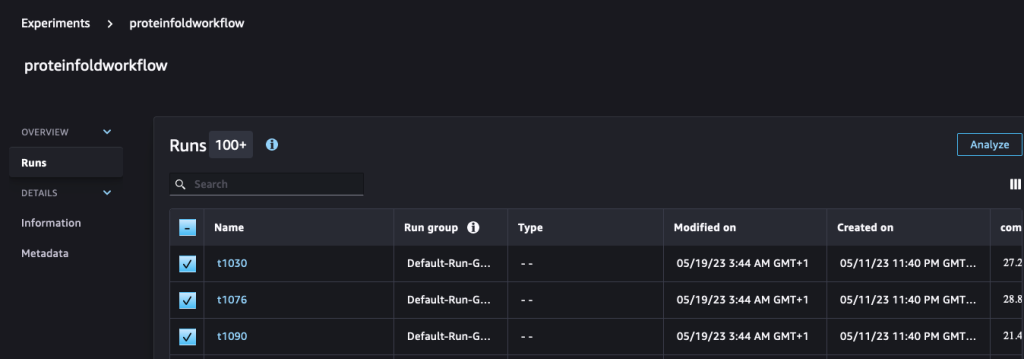
Καταγράφουμε επίσης τις μετρήσεις με τα πειράματα SageMaker ως νέες εκτελέσεις του ίδιου πειράματος που δημιουργήθηκαν από τη διοχέτευση:
from sagemaker.experiments.run import Run, load_run
metric_type='compare:'
experiment_name = 'proteinfoldworkflow'
with Run(experiment_name=experiment_name, run_name=input_name_1, sagemaker_session=sess) as run:
run.log_metric(name=metric_type + "rmsd_cur", value=rmsd_cur_one, step=1)
run.log_metric(name=metric_type + "rmds_fit", value=rmsd_fit_one, step=1)
run.log_metric(name=metric_type + "tm_score", value=tmscore_one, step=1)Στη συνέχεια αναλύουμε και οπτικοποιούμε αυτές τις διαδρομές στο Πειράματα σελίδα στο SageMaker Studio.
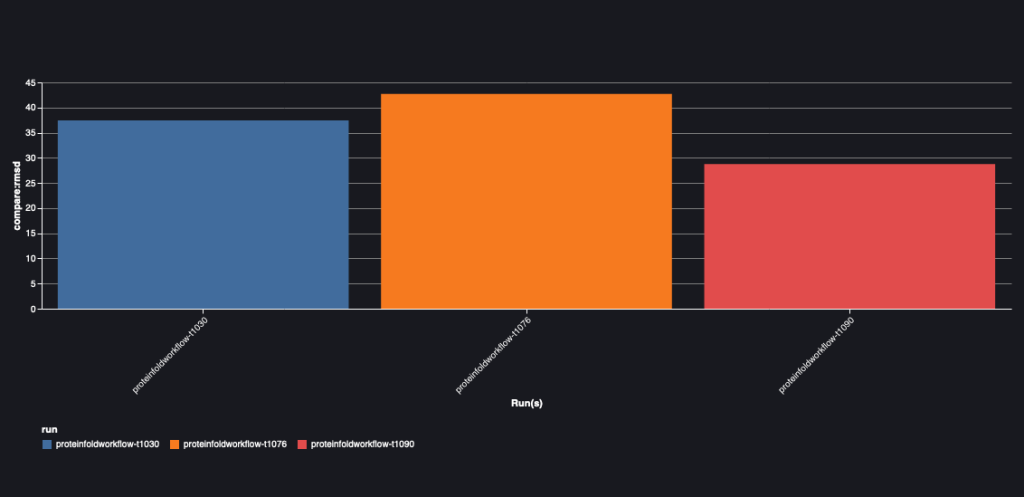
Το παρακάτω γράφημα απεικονίζει την τιμή RMSD μεταξύ AlphaFold και OpenFold για τις τρεις ακολουθίες: T1030, T1076 και T1090.
Συμπέρασμα
Σε αυτήν την ανάρτηση, περιγράψαμε πώς μπορείτε να χρησιμοποιήσετε το SageMaker Pipelines για να ρυθμίσετε και να εκτελέσετε ροές εργασιών αναδίπλωσης πρωτεϊνών με δύο δημοφιλείς αλγόριθμους πρόβλεψης δομής: AlphaFold2 και OpenFold. Επιδείξαμε μια αρχιτεκτονική λύσης με απόδοση τιμής πολλαπλών εργασιών που διαχωρίζει τις υπολογιστικές απαιτήσεις για τη δημιουργία MSA από την πρόβλεψη δομής. Επισημάναμε επίσης πώς μπορείτε να απεικονίσετε, να αξιολογήσετε και να συγκρίνετε τις προβλεπόμενες τρισδιάστατες δομές πρωτεϊνών στο SageMaker Studio.
Για να ξεκινήσετε με τις ροές εργασιών αναδίπλωσης πρωτεΐνης στο SageMaker, ανατρέξτε στο δείγμα κώδικα στο GitHub repo.
Σχετικά με τους συγγραφείς
 Michael Hsieh είναι Κύριος Αρχιτέκτονας Ειδικών Λύσεων AI/ML. Συνεργάζεται με πελάτες HCLS για να προωθήσει το ταξίδι τους ML με τις τεχνολογίες AWS και την τεχνογνωσία του στην ιατρική απεικόνιση. Ως μεταμόσχευση στο Σιάτλ, του αρέσει να εξερευνά τη μεγάλη μητρική φύση που έχει να προσφέρει η πόλη, όπως τα μονοπάτια πεζοπορίας, το καγιάκ στο SLU και το ηλιοβασίλεμα στον κόλπο Shilshole.
Michael Hsieh είναι Κύριος Αρχιτέκτονας Ειδικών Λύσεων AI/ML. Συνεργάζεται με πελάτες HCLS για να προωθήσει το ταξίδι τους ML με τις τεχνολογίες AWS και την τεχνογνωσία του στην ιατρική απεικόνιση. Ως μεταμόσχευση στο Σιάτλ, του αρέσει να εξερευνά τη μεγάλη μητρική φύση που έχει να προσφέρει η πόλη, όπως τα μονοπάτια πεζοπορίας, το καγιάκ στο SLU και το ηλιοβασίλεμα στον κόλπο Shilshole.
 Σιβάμ Πατέλ είναι αρχιτέκτονας λύσεων στην AWS. Προέρχεται από ένα υπόβαθρο στην Ε&Α και το συνδυάζει με τις επιχειρηματικές του γνώσεις για να λύσει περίπλοκα προβλήματα που αντιμετωπίζουν οι πελάτες του. Ο Shivam είναι πιο παθιασμένος με τους φόρτους εργασίας στη μηχανική μάθηση, τη ρομποτική, το IoT και τους υπολογιστές υψηλής απόδοσης.
Σιβάμ Πατέλ είναι αρχιτέκτονας λύσεων στην AWS. Προέρχεται από ένα υπόβαθρο στην Ε&Α και το συνδυάζει με τις επιχειρηματικές του γνώσεις για να λύσει περίπλοκα προβλήματα που αντιμετωπίζουν οι πελάτες του. Ο Shivam είναι πιο παθιασμένος με τους φόρτους εργασίας στη μηχανική μάθηση, τη ρομποτική, το IoT και τους υπολογιστές υψηλής απόδοσης.
 Χασάν Πουνουάλα είναι Ανώτερος Αρχιτέκτονας Λύσεων Specialist AI/ML στην AWS, ο Hasan βοηθά τους πελάτες να σχεδιάσουν και να αναπτύξουν εφαρμογές μηχανικής εκμάθησης στην παραγωγή στο AWS. Έχει πάνω από 12 χρόνια εργασιακής εμπειρίας ως επιστήμονας δεδομένων, επαγγελματίας μηχανικής μάθησης και προγραμματιστής λογισμικού. Στον ελεύθερο χρόνο του, ο Χασάν λατρεύει να εξερευνά τη φύση και να περνά χρόνο με φίλους και οικογένεια.
Χασάν Πουνουάλα είναι Ανώτερος Αρχιτέκτονας Λύσεων Specialist AI/ML στην AWS, ο Hasan βοηθά τους πελάτες να σχεδιάσουν και να αναπτύξουν εφαρμογές μηχανικής εκμάθησης στην παραγωγή στο AWS. Έχει πάνω από 12 χρόνια εργασιακής εμπειρίας ως επιστήμονας δεδομένων, επαγγελματίας μηχανικής μάθησης και προγραμματιστής λογισμικού. Στον ελεύθερο χρόνο του, ο Χασάν λατρεύει να εξερευνά τη φύση και να περνά χρόνο με φίλους και οικογένεια.
 Jasleen Grewal είναι Ανώτερη Εφαρμοσμένη Επιστήμονας στο Amazon Web Services, όπου συνεργάζεται με πελάτες AWS για την επίλυση προβλημάτων του πραγματικού κόσμου χρησιμοποιώντας μηχανική μάθηση, με ιδιαίτερη έμφαση στην ιατρική ακριβείας και τη γονιδιωματική. Έχει ισχυρό υπόβαθρο στη βιοπληροφορική, την ογκολογία και την κλινική γονιδιωματική. Είναι παθιασμένη με τη χρήση υπηρεσιών AI/ML και cloud για τη βελτίωση της φροντίδας των ασθενών.
Jasleen Grewal είναι Ανώτερη Εφαρμοσμένη Επιστήμονας στο Amazon Web Services, όπου συνεργάζεται με πελάτες AWS για την επίλυση προβλημάτων του πραγματικού κόσμου χρησιμοποιώντας μηχανική μάθηση, με ιδιαίτερη έμφαση στην ιατρική ακριβείας και τη γονιδιωματική. Έχει ισχυρό υπόβαθρο στη βιοπληροφορική, την ογκολογία και την κλινική γονιδιωματική. Είναι παθιασμένη με τη χρήση υπηρεσιών AI/ML και cloud για τη βελτίωση της φροντίδας των ασθενών.
- SEO Powered Content & PR Distribution. Ενισχύστε σήμερα.
- PlatoData.Network Vertical Generative Ai. Ενδυναμώστε τον εαυτό σας. Πρόσβαση εδώ.
- PlatoAiStream. Web3 Intelligence. Ενισχύθηκε η γνώση. Πρόσβαση εδώ.
- PlatoESG. Αυτοκίνητο / EVs, Ανθρακας, Cleantech, Ενέργεια, Περιβάλλον, Ηλιακός, Διαχείριση των αποβλήτων. Πρόσβαση εδώ.
- BlockOffsets. Εκσυγχρονισμός της περιβαλλοντικής αντιστάθμισης ιδιοκτησίας. Πρόσβαση εδώ.
- πηγή: https://aws.amazon.com/blogs/machine-learning/build-protein-folding-workflows-to-accelerate-drug-discovery-on-amazon-sagemaker/
- :έχει
- :είναι
- :δεν
- :που
- $UP
- 1
- 10
- 100
- 12
- 3d
- 7
- 9
- a
- Σχετικα
- AC
- επιταχύνουν
- πρόσβαση
- πρόσβαση
- ακρίβεια
- ακριβής
- απεριοδικός
- προσθέτω
- θετός
- εκ των προτέρων
- προκαταβολές
- συγκινητικός
- Μετά το
- πάλι
- κατά
- AI / ML
- αλγόριθμος
- αλγόριθμοι
- ευθυγραμμία
- Όλα
- επιτρέπουν
- επιτρέπει
- κατά μήκος
- Επίσης
- Amazon
- Amazon Sage Maker
- Στούντιο Amazon SageMaker
- Amazon υπηρεσίες Web
- an
- ανάλυση
- αναλύσει
- και
- Άλλος
- κάθε
- εφαρμογές
- εφαρμοσμένος
- αρχιτεκτονική
- ΕΙΝΑΙ
- ΠΕΡΙΟΧΗ
- επιχειρήματα
- AS
- εκτίμηση
- At
- αυτομάτως
- διαθέσιμος
- μέσος
- μακριά
- AWS
- πίσω
- φόντο
- βάση
- βασίζονται
- Κόλπος
- BE
- επειδή
- γίνεται
- πριν
- Αρχή
- είναι
- εκτός
- ΚΑΛΎΤΕΡΟΣ
- Καλύτερα
- μεταξύ
- Δισεκατομμύριο
- δισεκατομμύρια
- βιοϊατρικής
- βιοφάρμα
- Μπλοκ
- σώμα
- και οι δύο
- φέρω
- Φέρνοντας
- ευρύς
- χτίζω
- Κτίριο
- επιχείρηση
- by
- κλήση
- που ονομάζεται
- CAN
- υποψήφιος
- υποψηφίους
- δυνατότητες
- ικανός
- ο οποίος
- αλλαγή
- Κανάλι
- Διάγραμμα
- επιλογή
- Πόλη
- τάξη
- Κλινικός
- Κλεισιμο
- Backup
- υπηρεσίες cloud
- συστάδα
- κωδικός
- βάση κώδικα
- κώδικες
- συνεργάζομαι
- συνδυασμός
- συνδυάζει
- έρχεται
- εμπορικός
- Κοινός
- επικοινωνούν
- συγκρίνουν
- σύγκριση
- σύγκριση
- σύμφωνος
- ανταγωνισμός
- πλήρης
- Ολοκληρώθηκε το
- Ολοκληρώνει
- συγκρότημα
- συστατικό
- εξαρτήματα
- Χημική ένωση
- υπολογισμός
- Υπολογίστε
- χρήση υπολογιστή
- διαμόρφωση
- κατασκευάσει
- δόμηση
- Δοχείο
- Περιέχει
- Κόστος
- εξοικονόμηση κόστους
- Δικαστικά έξοδα
- Ζευγάρι
- δημιουργία
- δημιουργήθηκε
- Τη στιγμή
- έθιμο
- Πελάτες
- DAG
- ημερομηνία
- διαχείριση δεδομένων
- επεξεργασία δεδομένων
- επιστήμονας δεδομένων
- βάση δεδομένων
- βάσεις δεδομένων
- Ημερομηνία
- βαθύς
- βαθιά μάθηση
- Προεπιλογή
- ορίζεται
- ορίζεται
- καθορίζοντας
- αποδεικνύουν
- κατέδειξε
- Εξάρτηση
- παρατάσσω
- Συμπληρωματικός
- περιγράφεται
- Υπηρεσίες
- σχεδιασμένα
- επιθυμητή
- λεπτομερής
- Προσδιορίστε
- καθορίζει
- Εργολάβος
- Ανάπτυξη
- διαφορετικές
- δύσκολος
- ανακάλυψη
- συζητήσουν
- Νόσος
- Ποικιλία
- διαιρούμενο
- Λιμενεργάτης
- κάτω
- κατεβάσετε
- φάρμακο
- Ναρκωτικά
- κατά την διάρκεια
- δυναμικός
- κάθε
- Νωρίτερα
- εύκολα
- Αποτελεσματικός
- είτε
- ενεργοποιήσετε
- τέλος
- οντότητες
- καταχώριση
- Περιβάλλον
- περιβάλλοντος
- αξιολογήσει
- ενδεχόμενος
- Κάθε
- παράδειγμα
- εξαίρεση
- εκτελέστηκε
- εκτέλεση
- υφιστάμενα
- ακριβά
- εμπειρία
- πείραμα
- πειράματα
- εξειδίκευση
- εξήγηση
- διερευνήσει
- Εξερευνώντας
- αντιμετωπίζουν
- Απέτυχε
- οικογένεια
- Χαρακτηριστικό
- Χαρακτηριστικά
- Αρχεία
- Αρχεία
- τελικός
- Τελικά
- Όνομα
- πρώτη φορά
- ταιριάζουν
- Ευελιξία
- εύκαμπτα
- Συγκέντρωση
- ακολουθήστε
- Εξής
- εξής
- Για
- μορφή
- φίλους
- από
- πλήρη
- πλήρως
- λειτουργικός
- περαιτέρω
- συγκεντρώνουν
- δημιουργεί
- γενεά
- γονιδιωματική
- παίρνω
- δεδομένου
- Go
- GPU
- γραφική παράσταση
- εξαιρετική
- σε μεγάλο βαθμό
- Ήμισυ
- χέρι
- χούφτα
- βλάψει
- Έχω
- he
- βαριά
- βοήθεια
- βοηθά
- εδώ
- Ψηλά
- υψηλού επιπέδου
- υψηλή απόδοση
- υψηλής ποιότητας
- υψηλότερο
- υψηλότερο
- Τόνισε
- του
- φιλοξενία
- ΩΡΕΣ
- Πως
- Πώς να
- Ωστόσο
- HTML
- http
- HTTPS
- Εκατοντάδες
- Αναγνώριση
- προσδιορίσει
- Idle
- if
- απεικονίζει
- εικόνα
- εικόνες
- Απεικόνιση
- εκτέλεση
- εισαγωγή
- βελτίωση
- βελτιώσεις
- in
- περιλαμβάνουν
- περιλαμβάνει
- Συμπεριλαμβανομένου
- ενσωματώνω
- ανεξάρτητος
- ατομικές
- πληροφορίες
- Υποδομή
- εισαγωγή
- είσοδοι
- μέσα
- εγκαθιστώ
- παράδειγμα
- διαδραστικό
- διαδραστικός
- περιβάλλον λειτουργίας
- σε
- εισαγάγει
- IoT
- IT
- ΤΟΥ
- Δουλειά
- Θέσεις εργασίας
- ταξίδι
- jpg
- μόλις
- διατηρούνται
- Κλειδί
- κλωτσήσει
- Ξέρω
- γνώση
- γνωστός
- Επίθετο
- Αφάνεια
- αργότερο
- ξεκινήσει
- στρώμα
- στρώματα
- Οδηγεί
- μάθηση
- ελάχιστα
- ας
- Επίπεδο
- Βιβλιοθήκη
- ζωή
- Μου αρέσει
- πιθανότητα
- γραμμές
- ΣΥΝΔΕΣΜΟΙ
- τοπικά
- τοποθεσία
- θέσεις
- κούτσουρο
- ξύλευση
- Μακριά
- αγαπά
- χαμηλότερα
- χαμηλότερο
- μηχανή
- μάθηση μηχανής
- κάνω
- διαχείριση
- διαχειρίζεται
- διαχείριση
- διαχείριση
- χειροκίνητα
- Ενδέχεται..
- McKinsey
- μηχανισμός
- ιατρικών
- ιατρική
- Μεταδεδομένα
- μέθοδος
- μέθοδοι
- Metrics
- εκατομμύρια
- ML
- Τρόπος
- μοντέλο
- μοντελοποίηση
- μοντέλα
- Παρακολούθηση
- παρακολούθηση
- περισσότερο
- πλέον
- μητέρα
- ΤΟΠΟΘΕΤΗΣΗ
- πολύ
- πολλαπλούς
- όνομα
- Φύση
- Ανάγκη
- χρειάζονται
- δικτύωσης
- δίκτυα
- νευρωνικά δίκτυα
- Νέα
- νέος στόχος
- επόμενη
- ΝΙΗ
- ιδιαίτερα
- σημειωματάριο
- τώρα
- αριθμός
- of
- off
- προσφορά
- προσφορές
- Καλά
- on
- Κατα παραγγελια
- ONE
- αποκλειστικά
- επάνω σε
- λειτουργία
- βέλτιστη
- Βελτιστοποίηση
- Επιλογή
- or
- τάξη
- ΑΛΛΑ
- δικός μας
- παραγωγή
- επί
- σελίδα
- Παράλληλο
- παράμετρος
- παράμετροι
- μέρος
- Ειδικότερα
- Συνεργάτες
- passieren
- πέρασε
- παθιασμένος
- μονοπάτι
- ασθενής
- pacientes
- πρότυπο
- για
- επίδοση
- αγωγού
- Πλάτων
- Πληροφορία δεδομένων Plato
- Πλάτωνα δεδομένα
- Σημείο
- Δημοφιλής
- κατοικημένη περιοχή
- Θέση
- ανάγκη
- Ακρίβεια
- προβλέψει
- προβλεπόμενη
- προβλέποντας
- πρόβλεψη
- Προβλέψεις
- Προετοιμάστε
- προαπαιτούμενα
- παρόν
- προηγούμενος
- τιμή
- πρωταρχικός
- Κύριος
- Πριν
- ιεράρχηση
- Πρόβλημα
- προβλήματα
- διαδικασια μας
- Διεργασίες
- μεταποίηση
- Προϊόν
- παραγωγή
- Πρόγραμμα
- Πρόοδος
- υπόσχεση
- κατάλληλος
- Πρωτεΐνη
- Πρωτεΐνες
- παρέχουν
- παρέχεται
- παρέχει
- βάζω
- Python
- γρήγορα
- Ε & Α
- πραγματικός
- πραγματικό κόσμο
- πρόσφατος
- αναφέρεται
- περιοχές
- Σχέσεις
- παραμένουν
- αξιοσημείωτος
- επαναληπτός
- ΚΑΤ 'ΕΠΑΝΑΛΗΨΗ
- Αποθήκη
- εκπροσωπούνται
- εκπροσωπούν
- απαιτούν
- απαιτείται
- απαίτηση
- απαιτήσεις
- έρευνα
- ερευνητές
- Υποστηρικτικό υλικό
- αντίστοιχα
- με αποτέλεσμα
- Αποτελέσματα
- ρομποτική
- τρέξιμο
- τρέξιμο
- τρέχει
- s
- σοφός
- Αγωγοί SageMaker
- ίδιο
- οικονομία
- Οικονομίες
- Απεριόριστες δυνατότητες
- επεκτάσιμη
- Κλίμακα
- Επιστήμη
- Επιστήμονας
- επιστήμονες
- σκορ
- προσυμπτωματικού ελέγχου
- Εφαρμογές
- SDK
- Αναζήτηση
- Σιάτλ
- Δεύτερος
- Τμήμα
- δείτε
- σπόροι
- δει
- επιλογή
- αρχαιότερος
- Ακολουθία
- Σειρές
- υπηρεσία
- Υπηρεσίες
- σειρά
- Σέτς
- τον καθορισμό
- setup
- διάφοροι
- αυτή
- θα πρέπει να
- δείχνουν
- παρουσιάζεται
- Δείχνει
- τερματίστε
- σημαντικός
- παρόμοιες
- Απλούς
- απλοποιημένη
- ενιαίας
- So
- λογισμικό
- λύση
- Λύσεις
- SOLVE
- Πηγή
- ειδική
- ειδικός
- συγκεκριμένες
- ειδικά
- εξειδίκευση
- καθορίζεται
- Φασματοσκοπία
- δαπανήσει
- Στάδιο
- Εκκίνηση
- ξεκίνησε
- Ξεκινήστε
- ξεκινά
- Κατάσταση
- Βήμα
- Βήματα
- χώρος στο δίσκο
- αποθηκεύονται
- εξορθολογισμένη
- ισχυρός
- κατασκευαστικός
- δομή
- στούντιο
- υποβολή
- υποβάλουν
- υποβάλλονται
- επιτυχής
- τέτοιος
- κατάλληλος
- Ηλιοβασίλεμα
- προσθήκη
- Υποστηρίζει
- σύστημα
- συστήματα
- τραπέζι
- Πάρτε
- παίρνει
- λήψη
- στόχος
- στόχους
- ομάδες
- Τεχνολογίες
- πρότυπο
- πρότυπα
- όροι
- Δοκιμές
- ότι
- Η
- Η Πηγη
- τους
- Τους
- τότε
- επομένως
- Αυτοί
- αυτοί
- Τρίτος
- αυτό
- εκείνοι
- χιλιάδες
- τρία
- Μέσω
- διακίνηση
- ώρα
- χρονοβόρος
- προς την
- μαζι
- εργαλεία
- κορυφή
- Ιχνηλασιμότητα
- τροχιά
- παραδοσιακός
- Τρένο
- εκπαιδευμένο
- Εκπαίδευση
- μετασχηματιστής
- αληθής
- δύο
- τύπος
- τυπικός
- συνήθως
- ui
- καταλαβαίνω
- κατανόηση
- Δυστυχώς
- άγνωστος
- ενημερώθηκε
- Φορτώθηκε
- us
- χρήση
- μεταχειρισμένος
- Χρήστες
- Η εμπειρία χρήστη
- Διεπαφής χρήστη
- Χρήστες
- χρησιμοποιεί
- χρησιμοποιώντας
- επικύρωση
- αξία
- ποικιλία
- διάφορα
- πολύ
- μέσω
- οραματισμός
- ήταν
- Τρόπος..
- we
- ιστός
- διαδικτυακές υπηρεσίες
- Web-based
- βάρος
- ΛΟΙΠΌΝ
- πότε
- Ποιό
- ενώ
- Wikipedia
- θα
- με
- εντός
- χωρίς
- Εργασία
- ροής εργασίας
- ροές εργασίας
- λειτουργεί
- κόσμος
- θα
- γραπτή
- ακτινογραφία
- χρόνια
- Εσείς
- Σας
- zephyrnet